近年来,随着数据量的爆炸式增长,传统存储介质的局限性日益显现。DNA作为一种天然的信息载体,因其极高的存储密度、出色的抗电磁干扰能力以及长期稳定性,逐渐成为冷数据存储领域的理想选择,尤其适用于那些需要长期归档且不常访问的数据。然而,现有的DNA存储技术大多依赖于序列合成的顺序存储方式,难以支持高频访问和动态修改,限制了其在热数据处理方面的应用,无法满足快速随机访问和灵活编辑的需求。
针对这一挑战,南京邮电大学柔性电子全国重点实验室、化学与生命科学学院晁洁教授团队近期提出了一种基于DNA折纸纳米结构的链式数据存储系统(DNA Origami-based Linked Data Storage, DONLDS)。该研究通过将链表数据结构与DNA纳米技术相结合,构建了一种新型的存储架构,能够高效存储多种类型的数据,包括英文文本、数字信息和中文内容,并支持数据的动态插入与删除操作。这一成果为下一代信息存储技术的发展提供了新的思路。相关研究论文已发表在《Nature Communications》上,题为“Linked data storage using DNA origami nanostructures”。
科研团队受计算机科学中链表概念的启发,设计并构建了三种形态各异的DNA折纸纳米结构作为信息存储的基本单元,分别为三角形(TDON)、矩形(RDON)和十字形(CDON)节点。每种结构均集成数据与指针两大功能模块:数据域借助链霉亲和素与生物素的特异性结合,将带有二进制编码的数据链精确锚定于节点上;指针域则通过预设的DNA单链序列,与可编程的“指令链”发生互补配对,从而实现节点之间的可控连接或断开。这一机制借鉴了计算机链式存储的思想,使得数据不必局限于连续空间,能够根据信息量动态扩展,在数据更新时也无需整体迁移。
基于该DNA折纸链式存储系统(DONLDS),研究团队首先利用TDON节点对26个英文字母进行了编码,并成功构建出“HELLO WORLD”这一字符串的信息链。定量检测显示,链霉亲和素能够稳定、精准地结合在预设的数据位点上,各个TDON节点的信息存储准确率在91.17±0.86%至95.64±2.05%之间浮动。该组数据表明,该编码策略不仅具备高准确性,且重复性良好,为其在分子级数据存储领域的实际推广提供了可靠依据。
进一步实验显示,该存储架构支持灵活的动态信息编辑。研究团队以存储内容为“DNA helix 1953”的链表为模板,通过精准移除“helix”与“1953”节点,并嵌入“storage”与“1988”节点,成功将其重构为“DNA storage 1988”。整个编辑过程无需遍历所有数据结构,显著提升了操作效率。在24组平行样本的验证中,所有数据均得以完整恢复,充分证明了该编辑方式的准确性与鲁棒性,表明DNA纳米技术所构建的数据处理系统在信息存储与编辑方面展现出可观的应用前景。
该工作得到了国家重点研发计划、国家自然科学基金、江苏省自然科学基金前沿技术项目及新基石科学基金会的联合支持。柔性电子全国重点实验室的晁洁教授为论文的通讯作者,南京邮电大学博士研究生张晨昊为论文第一作者。谢茉副教授,汪联辉教授樊春海院士为该研究工作做出了重要贡献。
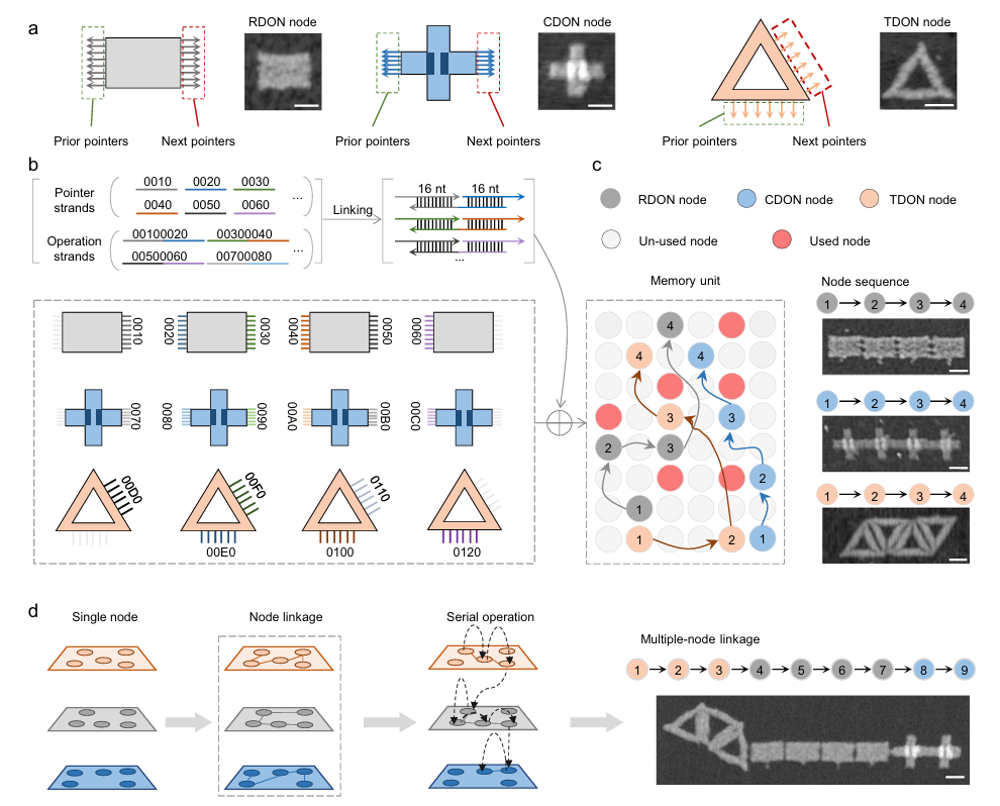
基于DNA折纸纳米结构的链式数据存储(DONLDS)系统概述图
原文链接:https://www.nature.com/articles/s41467-025-66274-x
撰稿:王君珂 编辑:彭芃 初审:张晨昊 审核:罗志敏

